Inverted Repeat
From Wikipedia, the free encyclopedia
Ein inverted repeat (engl. für ‚umgekehrte Wiederholung‘) ist eine Nukleotidsequenz in einer doppelsträngigen Nukleinsäure, die sich auf dem anderen Strang in umgekehrter Reihenfolge wiederholt. Aufgrund der Basenpaarung kommt ein inverted repeat strangabwärts auf demselben Strang revers komplementär vor. Befinden sich die inverted repeats an beiden 5'- oder beiden 3'-Enden einer doppelsträngigen Nukleinsäure, werden sie als inverted terminal repeats oder terminal inverted repeats (TIRs) bezeichnet.
Eigenschaften
Inverted repeats werden von manchen Viren wie Retroviren oder das Adeno-assoziierte Virus[1] zur Insertion des viralen Genoms in das Genom des Wirts verwendet. Daneben kommen sie bei Insertionssequenzen, Transposons[2] und Miniature Inverted-repeat Transposable Elements[3] vor. Weiterhin kommen inverted repeats – allerdings ohne Nukleotide dazwischen – in den palindromischen Erkennungssequenzen von Restriktionsendonukleasen des Typs II vor. Teilweise kommen inverted repeats als tandem repeats in mehrfachen Wiederholungen in einer Nukleotidsequenz vor.
Inverted repeats sind oftmals ein Ort für Rekombination,[4] teilweise durch Ausbildung von Sekundärstrukturen wie Haarnadelstrukturen oder kreuzförmigen Strukturen.[5] Weiterhin sind sie an der Genamplifikation beteiligt und erhöhen dadurch die evolutionäre Anpassungsfähigkeit.[6] Gleichzeitig sind sie aber auch eine Quelle für Mutationen, die in Gendefekten resultieren können.[7]
Datenbanken für inverted repeats sind beispielsweise non-B DB,[8][9] Inverted Repeats Database,[10][11] P-MITE,[12][13] EMBOSS[14] und Palindrome Analyser,[15][16]
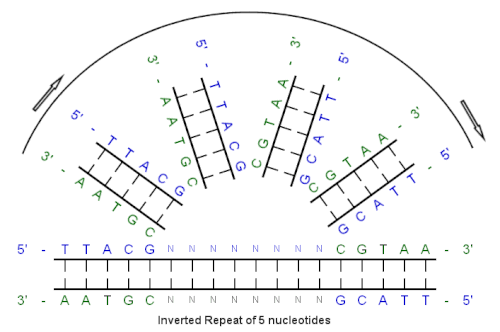
Beispiel
- 5’-TTACGnnnnnnCGTAA-3’
- 3’-AATGCnnnnnnGCATT-5’