ChIP-Seq
From Wikipedia, the free encyclopedia
Die ChIP-Seq (von engl. Chromatin ImmunoPrecipitation DNA-Sequencing) ist eine biochemische Methode zur Bestimmung von Protein-DNA-Interaktionen. Die ChIP-Seq ist eine Kombination aus einer Chromatin-Immunpräzipitation und der DNA-Sequenzierung im Hochdurchsatz.[1][2] DNA-Protein-Interaktionen kommen bei Bindungssequenzen für Transkriptionsfaktoren an Promotoren, Enhancer, Repressoren, Silencer, Isolatoren sowie bei Bindungssequenzen für die DNA-Replikation vor.[3]
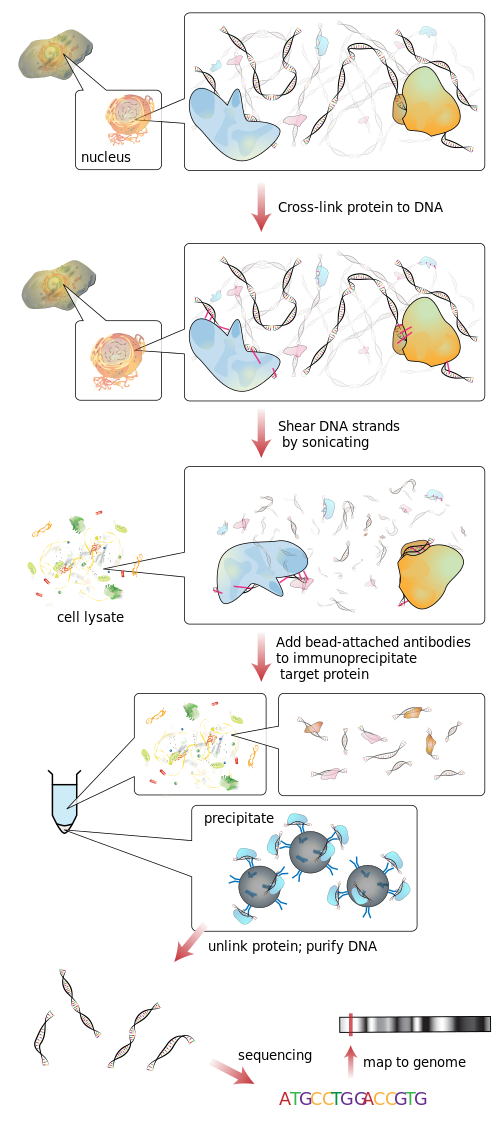
Eigenschaften
Das gereinigte rekombinante Protein wird mit der DNA vermischt oder in vivo gebunden, mit Formaldehyd reversibel quervernetzt. Anschließend erfolgt eine Fragmentierung per Ultraschall und eine Immunpräzipitation der vernetzten Protein-DNA-Komplexe mit einem Antikörper gegen das rekombinante Protein oder sein Protein-Tag. Abschließend erfolgt die thermische Freisetzung der DNA und eine DNA-Sequenzierung im Hochdurchsatz.
Eine Alternativmethode ist die ChIP-on-Chip, welche die Chromatin-Immunpräzipitation mit einer Hybridisierung mit einem DNA-Microarray (synonym DNA-Chip) verbindet. Durch eine parallele Verwendung beider Methoden können systematische Fehler der Methoden teilweise gemindert werden. Im Gegensatz zum ChIP-on-Chip erhöhen sich bei der ChIP-Seq die Kosten bei einer Erhöhung der Sensitivität, da hierbei viele Sequenziervorgänge erforderlich werden. Eine Variante der ChIP-Seq ist die Competition ChIP-Seq mit der untersucht wird, ob zwei Transkriptionsfaktoren um die Bindung an DNA-Sequenzen kompetieren.[4]
Verwandte Methoden ohne Immunpräzipitation sind die DNAse-Seq und die FAIRE-Seq (formaldehyde-assisted isolation of regulatory elements with high-throughput sequencing), welche entfaltete Regionen der DNA sequenzieren, an denen eine Regulation der Genexpression stattfindet.[5] Die ChIRP-Seq ist eine ChIP-Seq, bei der DNA-bindende RNA selektiv nachgewiesen werden kann.[6]
Die Kombination eines Nuclease Protection Assays mit einer ChIP-Seq wird als ChIP-Exo bezeichnet, bei der von Proteinen unbedeckte DNA-Bereiche durch eine Exonuklease aus dem Bakteriophagen λ verdaut werden, die übrigen dagegen sequenziert werden.[7]
