Riboviria
From Wikipedia, the free encyclopedia
| Riboviria | ||
|---|---|---|
 | ||
| Taxonomía | ||
| Dominio: | Riboviria | |
| Reinos | ||
| ||
Riboviria es un dominio vírico introducido por el Comité Internacional de Taxonomía de Virus para la clasificación de los virus que agrupa a los virus ARN y los virus retrotranscritos.[1] Comprende a los grupos III, IV, V, VI y VII de la clasificación de Baltimore. La primera parte de su nombre, Ribo proviene de ácido ribonucleico (ARN).[2] Se divide en dos reinos Pararnavirae que incluye los virus retrotranscritos y Orthornavirae que incluye los virus de ARN, exceptuando los virus satélites de ARN que se clasifican sin reino. Fue el primer dominio de virus creado, posteriormente se crearon cuatro dominios más que agrupan virus de ADN y otro de ARN que agrupa a los virusoides. El Comité Internacional de Taxonomía de Virus considera que este dominio es monofilético, sin embargo algunos análisis han demostrado que es parafilético de los virus de ADN y los organismos celulares con lo cual es controversial.[3]
Los virus de ARN se caracterizan por poseer una ARN polimerasa dependiente de ARN (RdRp) y los virus retrotranscritos por poseer una transcriptasa inversa (RT). La agrupación surge debido a que se cree que las ARN polimerasas dependientes de ARN y las transcriptasas inversas tanto celulares como víricas tienen un ancestro común.[4]
Estos virus y otros han sido prominentes a lo largo de la historia, incluido el virus del mosaico del tabaco, que fue el primer virus en ser descubierto. Muchos virus retrotranscritos se endogenizan notablemente en el genoma de su anfitrión como parte de su ciclo de replicación. Como resultado de eso, se estima que alrededor del 7-8% del genoma humano está compuesto por retrovirus endógenos.[5][4]


Las enfermedades causadas por virus de Riboviria se conocen desde gran parte de la historia registrada, aunque su causa solo se descubrió en los tiempos modernos. El virus del mosaico del tabaco se descubrió en 1898 y fue el primer virus en ser descubierto.[6] Los virus transmitidos por artrópodos han sido fundamentales en el desarrollo del control de vectores, que a menudo tiene como objetivo prevenir las infecciones víricas.[7] En la historia moderna, varios miembros del dominio han causado numerosos brotes de enfermedades, incluidos el COVID-19, la gripe, el resfriado común, el ébola, el dengue, etc. El VIH especialmente ha tenido efectos dramáticos en la sociedad, ya que causa una fuerte disminución en la esperanza de vida y un estigma significativo para las personas infectadas.[8][9]
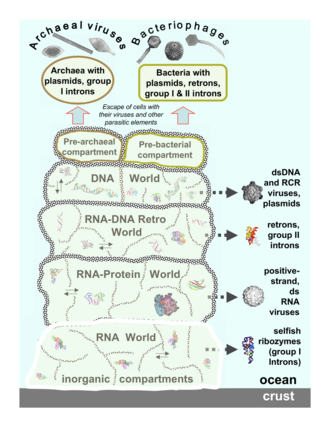
Durante mucho tiempo, no se pudo establecer una relación entre muchos virus de Riboviria debido a la alta mutación que sufren los virus de ARN. Con el desarrollo de la metagenómica vírica, se identificaron muchos virus de ARN adicionales, lo que ayudó a llenar los vacíos de sus relaciones. Esto llevó al establecimiento de Riboviria en 2018 para agrupar a todos los virus de ARN basado en análisis filogenéticos con los que estaban relacionados filogenéticamente.[4][2]
Un año después, todos los virus retrotranscritos se agregaron al dominio. Los reinos también se establecieron en 2019, separando las dos ramas de polimerasa dependientes de ARN. Cuando se creó el dominio, el sistema administrativo del ICTV incluyó erróneamente a los viroides y al género de virusoide Deltavirus que se eliminaron rápidamente en 2019 porque no codifican proteínas y se replican a través de ribozimas o polimerasas de ARN del huésped.[10]
Características



Todos los miembros de Riboviria contienen un gen que codifica una polimerasa dependiente de ARN, también llamada polimerasa dirigida por ARN. Hay dos tipos de polimerasas dependientes de ARN: ARN polimerasa dependiente de ARN (RdRp), también llamada ARN replicasa, que sintetiza ARN a partir de ARN y ADN polimerasa dependiente de ARN (RdDp), también llamada transcriptasa inversa (RT), que sintetiza ADN a partir de ARN. En una partícula de virus típica, llamada virión, la polimerasa dependiente de ARN se une al genoma vírico de alguna manera y comienza la transcripción del genoma vírico después de ingresar a una célula. Como parte del ciclo de vida de un virus, la polimerasa dependiente de ARN también sintetiza copias del genoma vírico como parte del proceso de creación de nuevos virus.[4]
Los virus que se replican a través de RdRp pertenecen a tres grupos en el sistema de clasificación de Baltimore, todos los cuales están en el reino Orthornavirae: los Virus ARN monocatenario positivo (ssARN+), los virus ARN monocatenario negativo (ssARN-) y los virus ARN bicatenario (dsARN). Los virus de ARN monocatenario positivo tienen genomas que pueden actuar funcionalmente como ARNm, y también se puede crear una hebra de sentido negativo para formar ARN bicatenario a partir del cual se transcribe el ARNm de la hebra negativa.[11] Los genomas de los virus de ARN monocatenario negativo y los de ARN bicatenario actúan como plantillas a partir de las cuales la RdRp crea el ARNm.[12][13]
Los virus retrotranscritos que se replican mediante una transcripción inversa pertenecen a dos grupos de la clasificación de Baltimore, ambos pertenecientes al reino Pararnavirae: los virus ARN monocatenario retrotranscrito (ssARN-RT), todos los cuales pertenecen al orden Ortervirales, y los virus ADN bicatenario retrotranscrito (dsADN-RT) que incluye la familia Caulimoviridae clasificada en el orden Ortervirales y la familia Hepadnaviridae clasificada separadamente. Los virus ssARN-RT tienen su genoma de sentido positivo transcrito por una RT para sintetizar una hebra de ADN complementario de sentido negativo (-cADN). La cadena de ARN + se degrada y luego se reemplaza por la RT con una cadena de ADN + para sintetizar una copia lineal de ADNdc del genoma vírico. Este genoma luego se integra en el ADN de la célula huésped.[14][15]
Para los virus dsADN-RT, se transcribe una hebra de ARN pregenómico + a partir del ADN circular relajado (rcADN), que a su vez es utilizado por una RT para transcribir una hebra de -cADN. La cadena de ARN + se degrada y se reemplaza de manera similar a los virus + ssADN-RT para sintetizar el rcADN. El genoma del ADNrc es posteriormente reparado por los mecanismos de reparación del ADN de la célula huésped para sintetizar un genoma de ADN circular cerrado covalentemente (ADNcc). El genoma integrado de los virus + ssARN-RT y el cccADN de los virus dsADN-RT son luego transcritos en ARN mensajero por la enzima ARN polimerasa II de la célula huésped.[14][15]
Los ribosomas de la célula huésped traducen el ARNm vírico para producir proteínas víricas. Para producir más virus, las polimerasas dependientes de ARN vírico utilizan copias del genoma vírico como plantillas para replicar el genoma vírico. Para los virus + ssARN, se crea un genoma intermedio de dsARN a partir del cual se sintetiza + ssARN a partir de la hebra negativa. Para los virus -ssARN, los genomas se sintetizan a partir de cadenas complementarias de sentido positivo. Los virus dsARN replican sus genomas a partir del ARNm sintetizando una hebra complementaria de sentido negativo para formar dsARN genómico. Para los virus dsADN-RT, el ARN pregenómico creado a partir del cccADN se retrotranscribe en nuevos genomas de dsADN. Para los virus + ssARN-RT, el genoma se replica a partir del genoma integrado. Después de la replicación y traducción, el genoma y las proteínas víricas se ensamblan en viriones completos, que luego abandonaran la célula huésped.[14][15]
Muchos virus retrotranscritos pueden integrarse en el genoma de su anfitrión. Estos virus se endogenizan como parte de su ciclo de replicación. Es decir, el ácido nucleico vírico se integra en el genoma del hospedador mediante la enzima retrovírica integrasa y el ARNm vírico se produce a partir de ese ADN. La endogenización es una forma de transferencia horizontal de genes entre organismos no relacionados y se estima que entre el 7 y el 8% del genoma humano está formado por retrovirus endógeno.[5] La endogenización también se puede utilizar para estudiar la historia evolutiva de estos virus, mostrando un período de tiempo aproximado cuando un virus se endogenizó por primera vez en el genoma del huésped, así como la tasa de evolución de los virus desde que se produjo la endogenización.[16][4] Los virus retrotranscritos con posterioridad originaron a los retrotransposones LTR por endogenización según análisis filogenéticos los cuales generalmente se transfieren de padres/madres a hijos. Estos retrotransposones son clasificados en las familias Pseudoviridae, Metaviridae y Belpaoviridae.[17]
Enfermedades e importancia ecológica
En el ser humano los virus de Riboviria son los causantes de la gripe, el resfriado común, el VIH, el sarampión, la rubeóla, la poliomielitis, las encefalitis, las hepatitis (exceptuando la D), la parotiditis, las fiebres hemorrágicas como el dengue o el ébola, el SARS como el COVID-19, las encefalitis, algunas diarreas y gastroenteritis.[9][8][18][19][20] En los animales causan la rabia, el moquillo, fiebres, estomatitis, leucemias, inmunodeficiencia, enfermedades respiratorias e intestinales, diarreas, etc.[19][21][22][23][24] En las plantas infectan todos los cultivos de importancia económica y pueden causar daños importantes a la productividad agrícola. También pueden causar la muerte de ciertas especies de árboles.[25] En hongos puede resultar de mayor importancia las infecciones a setas que son de importancia alimentaria y en los hongos microscópicos pueden ayudar a regular la población de parásitos, mohos o a la derivación vírica, también llamada lisis: un proceso por el cual el material órganico consumido por el huésped es liberado de vuelta al ambiente con la muerte y roptura de la membrana celular.[26] En protistas suelen regular la población de algunos protozoos como el parásito Giardia y ayudan a evitar la proliferación de algas. En bacterias y arqueas pueden ayudar a regular la población de la microbiota, parásitos o a la lisis. Especialmente estos últimos parecen desempeñar un papel importante en la controlación de la población bacteriana del suelo siendo los virus de ARN más predominantes en el suelo.[27][28]
Taxonomía
La taxonomía propuesta por el Comité Internacional de Taxonomía de Virus y otros estudios es la siguiente. También se indica su tipo de genoma:[1][29]
- Dominio Riboviria
- Reino Pararnavirae
- Familia Hepadnaviridae (ADN bicatenario retrotranscrito)
- Orden Ortervirales (ARN monocatenario retrotranscrito y ADN bicatenario retrotranscrito)
- Reino Orthornavirae
- Filo Lenarviricota (ARN monocatenario positivo)
- Filo Duplornaviricota (ARN bicatenario)
- Filo Pisuviricota (ARN monocatenario positivo y ARN bicatenario)
- Filo Kitrinoviricota (ARN monocatenario positivo)
- Filo Negarnaviricota (ARN monocatenario negativo)
- Filo Ambiviricota (ARN monocatenario negativo)
- Filo Artimaviricota (ARN bicatenario)
- Filo Taraviricota (ARN monocatenario positivo y ARN bicatenario)
- Filo Arctoviricota (ARN monocatenario negativo)
- Filo Paraxenoviricota (ARN monocatenario positivo)
- Filo Pomiviricota (ARN monocatenario positivo)
- Filo Wamoviricota (ARN monocatenario positivo)
- Reino Pararnavirae
- Órdenes y familias de colocación incierta (ARN monocatenario positivo)
- Familia Tonesaviridae
- Orden Tombendovirales
- Familia Pamosaviridae
- Familia Sarthroviridae
- Familia Tomosaviridae
Se ha sugerido que el filo Duplornaviricota debe ser dividido en tres filos separados. Los filos Taraviricota, Arctoviricota, Pomiviricota, Paraxenoviricota y Wamoviricota fueron descubiertos mediante muestras metagenómicas en los océanos y probablemente solo infecten microorganismos marinos.[29] El filo Artimaviricota fue descubierto en aguas termales ácidas e infectan bacterias termoacidofilas.[30]